Page 40 - 南京医科大学学报自然科学版
P. 40
第43卷第4期
·478 · 南 京 医 科 大 学 学 报 2023年4月
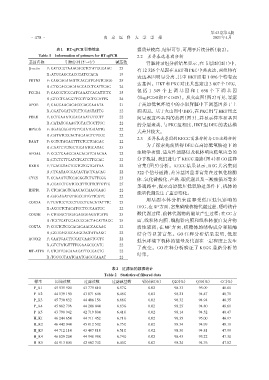
表1 RT⁃qPCR引物信息 据质量较高、结果可靠,可用于后续分析(表2)。
Table 1 Information of primers for RT⁃qPCR 2.2 差异表达基因分析
基因名称 引物序列(5′→3′) 碱基数 肾脏转录组分析结果显示,在韦恩图(图1)中,
β⁃actin F:CATCCGTAAAGACCTCTATGCCAAC 25
有12 326个基因在HKT和PKC中共表达,两组特有
R:ATGGAGCCACCGATCCACA 19
表达基因明显分离,其中 HKT 组有 1 096 个特有表
PRTN3 F:CAGCAGAAGTTCACCATCAGTCAGG 25
达基因。HKT 和 PKC 对比共鉴定出 3 007 个 DEG,
R:CTGGAGGAGAAGCACGTCATTGAG 24
包 括 1 349 个 上 调 基 因 和 1 658 个 下 调 基 因
FCGR4 F:CACCGTGGCATCAAATCACATTCTG 25
(|log2FC|>0和P < 0.05)。从火山图(图2)可见,暴露
R:GTCCTGAGGTTCCTTGCTCCATTG 24
APOE F:GAGGAACAGACCCAGCAAATA 21 于高原低氧环境中的小鼠肾脏中下调基因多于上
R:CGATGCATGTCTTCCACTATTG 22 调基因。基于火山图中DEG,在PKC组与HKT组之
PRLR F:CCTGAAATCCACAAATGTCGTT 22 间呈现这些基因的热图(图 3),并显示样本和基因
R:CATATGGAAGTGTACTGCTTGC 22 的分层聚类,与 PKC 组相比,HKT 组 DEG 的表达模
HPGDS F:AGAGCGGATGTTCAATGAATTG 22
式差异较大。
R:GATATCCCAGTAGAAGTCTGCC 22
2.3 差异表达基因的KEGG富集分析与GO注释分析
BAAT F:GGTGTAGAGTTTCTCCTGAGAC 22
为了探索先前所得 DEG 在高原低氧胁迫下的
R:CAATCTCTGCTCCAATGCATAC 23
生物学功能、适应性通路以及机体响应低氧应急的
APOA4 F:GGGTGAAGGAAGAGATCAAGAA 22
分子机制,我们进行了KEGG通路(图4)和GO注释
R:GTGTGTTGATCTGATCTTGCAG 22
RXRB F:TGACCTACTCGTGTCGTGATAA 22 富集(图 5)分析。KEGG 结果显示,DEG 共富集到
R:CTGATAGCGACAGTACTGACAG 22 322 个信号通路,差异基因显著富集在过氧化物酶
CYCS F:CCAAATCTCCACGGTCTGTTCGG 23 体、氧化磷酸化、产热、碳代谢以及三羧酸循环等多
R:CCAGGTGATGCCTTTGTTCTTGTTG 25
条通路中,提示高原低压低氧胁迫条件下,机体的
HSPB1 F:CTCACAGTGAAGACCAAGGAAG 22
能量代谢发生了重要变化。
R:GAGAGATGTAGCCATGTTCGTC 22
用基因本体分析来注释受低压低氧影响的
COX5A F:TGATGCTCGCTGGGTGACATATTTC 25
DEG,在BP方面,富集磷酸核糖代谢过程、嘌呤核苷
R:ACCGTCTACATGCTCGCAATGC 22
酸代谢过程、前体代谢物的能量产生过程;在CC方
COX5B F:CTGGGCTGGAGAGGGAGATCATG 23
R:TGCTGATGGACGGGACTAGATTAGG 25 面,线粒体内膜、细胞器内膜和线粒体蛋白复合物
COX7A F:CCGTGTGGCAGAGAAGCAGAAG 22 活性较强;在 MF 方面,核糖体的结构成分和辅酶
R:GCCCAGCCCAAGCAGTATAAGC 22 结合等显著富集。GO 注释分析结果表明,低压
ACOX2 F:CAATGACTTCCATCAAGTGGTG 22
低氧环境下机体的能量及代谢在一定程度上发生
R:GTCTATGTTTTCGAAGCCCATC 22
了改变。GO 注释分析验证了 KEGG 通路分析的
MT⁃ATP8 F:CTCATCACAAACATTCCCACTG 22
结果。
R:TGGGGTAATGAATGAGGCAAAT 22
表2 过滤后的数据统计
Table 2 Statistics of filtered data
样本 原始读数 过滤读数 过滤碱基数 错误率(%) Q20(%) Q30(%) GC(%)
P_K1 45 535 920 43 775 810 6.57G 0.02 98.33 95.09 48.60
P_K2 44 139 150 43 071 646 6.46G 0.02 98.21 94.47 48.71
P_K3 45 730 632 44 406 156 6.66G 0.02 98.32 94.94 48.35
P_K4 45 882 796 44 208 044 6.63G 0.02 98.25 94.80 48.60
P_K5 43 798 942 42 719 804 6.41G 0.02 98.14 94.52 48.47
H_K1 46 244 654 44 711 452 6.71G 0.02 98.35 95.00 46.97
H_K2 46 442 944 45 012 502 6.75G 0.02 98.34 94.99 48.19
H_K3 44 712 114 43 407 818 6.51G 0.02 98.30 94.81 47.99
H_K4 46 629 204 44 948 988 6.74G 0.02 98.43 95.22 47.30
H_K5 44 913 840 42 662 742 6.40G 0.02 98.24 94.76 47.82