Page 38 - 南京医科大学自然版
P. 38
第45卷第10期
·1406 · 南 京 医 科 大 学 学 报 2025年10月
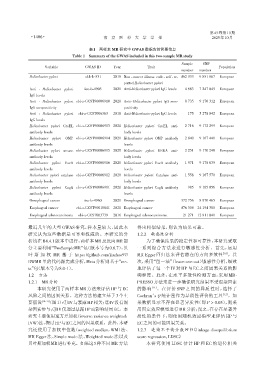
表1 两样本 MR 研究中 GWAS 数据库的简要信息
Table 1 Summary of the GWAS included in this two⁃sample MR study
Sample SNP
Variable GWAS ID Year Trait Population
number number
Helicobacter pylori ukb⁃b⁃531 2018 Non ⁃ cancer illness code,self ⁃ re⁃ 462 933 9 851 867 European
ported Helicobacter pylori
Anti ⁃ Helicobacter pylori ieu⁃b⁃4905 2021 Anti⁃Helicobacter pylori IgG levels 4 683 7 247 045 European
IgG levels
Anti ⁃ Helicobacter pylori ebi⁃a⁃GCST90006910 2020 Anti ⁃ Helicobacter pylori IgG sero⁃ 8 735 9 170 312 European
IgG seropositivity positivity
Anti ⁃ Helicobacter pylori ebi⁃a⁃GCST006363 2018 Anti⁃Helicobacter pylori IgG levels 175 5 278 042 European
IgG levels
Helicobacter pylori GroEL ebi⁃a⁃GCST90006913 2020 Helicobacter pylori GroEL anti⁃ 2 716 9 172 299 European
antibody levels body levels
Helicobacter pylori OMP ebi⁃a⁃GCST90006914 2020 Helicobacter pylori OMP antibody 2 640 9 167 440 European
antibody levels levels
Helicobacter pylori urease ebi⁃a⁃GCST90006915 2020 Helicobacter pylori UREA anti⁃ 2 251 9 170 248 European
antibody levels body levels
Helicobacter pylori VacA ebi⁃a⁃GCST90006916 2020 Helicobacter pylori VacA antibody 1 571 9 178 635 European
antibody levels levels
Helicobacter pylori catalase ebi⁃a⁃GCST90006912 2020 Helicobacter pylori Catalase anti⁃ 1 558 9 167 570 European
antibody levels body levels
Helicobacter pylori CagA ebi⁃a⁃GCST90006911 2020 Helicobacter pylori CagA antibody 985 9 165 056 European
antibody levels levels
Oesophageal cancer ieu⁃b⁃4960 2021 Oesophageal cancer 372 756 8 970 465 European
Esophageal cancer ebi⁃a⁃GCST90018841 2021 Esophageal cancer 476 306 24 194 380 European
Esophageal adenocarcinoma ebi⁃a⁃GCST003739 2016 Esophageal adenocarcinoma 21 271 12 911 041 European
最近几年的大型 GWAS 研究,样本量较大,因此本 得出相似结果,则认为结果可靠。
研究认为这些数据是可靠和权威的。本研究的分 1.2.2 敏感性分析
析均在R4.4.1版本中进行,两样本MR及反向MR部 为了确保结果的稳定性和可靠性,本研究采取
分主要利用“TwoSampleMR”包(版本号为 0.6.7),贝 一系列综合方法来进行敏感性分析。首先,运用
叶 斯 加 权 MR 基 于 https://github.com/jiazhao97/ MR Egger 回归法来评估潜在的方向多效性 [10] 。其
BWMR里的代码源完成分析,Meta分析则基于“me⁃ 次,采用“留一法”(leave⁃one⁃out)敏感性分析,细致
ta”包(版本号为8.0⁃1)。 地评估了每一个 IV 对 HP 与 EC 之间因果关系的影
1.2 方法 响程度。此外,在水平多效性检测方面,采用 MR⁃
1.2.1 MR分析 PRESSO方法来进一步确保研究结果不受混杂因素
本研究使用了两样本MR方法来评估HP与EC 的影响 [12] 。在评价 SNP 之间的异质性时,选择了
风险之间的因果关系。这种方法的建立基于3个主 Cochran’s Q 统计量作为异质性评价的工具 [13] 。如
要假设 [10-11] 果数据显示不存在显著异质性(即 P > 0.05),则采
(图1):①IV与暴露HP相关;②IV没有混
杂因素参与;③IV仅通过暴露HP而影响结局EC。本 用固定效应模型进行MR分析;反之,在存在显著异
研究主要使用逆方差加权(inverse variance weighted, 质性的条件下,则使用随机效应模型来评估 HP 与
IVW)法,探讨HP与EC之间的因果联系。此外,本研 EC之间的可能因果关系。
究还使用了加权中位数(weighted median,WM)法、 1.2.3 连锁不平衡分数回归(linkage disequilibrium
MR Egger 法、Simple mode 法、Weighted mode 法以及 score regression,LDSC)
贝叶斯加权MR进行补充。如果这5种不同 MR 方法 本研究使用 LDSC 估计 HP 和 EC 的遗传相关